Brûler la chandelle par les deux bouts : élimination des extrémités des chromosomes chez la paramécie
Longtemps considéré comme une curiosité biologique, l’élimination programmée d’ADN est en réalité un phénomène répandu, observé chez des centaines de milliers d’espèces, et concerne des segments de chromosomes, voire des chromosomes entiers, au cours de la différenciation des cellules somatiques. Dans une étude publiée dans BMC Biology, les scientifiques révèlent que les extrémités des chromosomes germinaux chez la paramécie sont eliminées par un mécanisme inédit, dont les bases moléculaires restent encore à élucider.
Chez de nombreux eucaryotes, le génome n’est pas une entité figée : il peut être remodelé au cours du développement par l’élimination programmée de portions d’ADN. Ce phénomène, appelé élimination programmée d’ADN, témoigne de la grande plasticité des génomes et soulève des questions fondamentales sur les mécanismes qui le contrôlent.
Un génome remodelé à chaque génération chez la paramécie
Les ciliés, dont fait partie la paramécie, constituent un modèle particulièrement intéressant pour étudier ce processus. Chez ces organismes unicellulaires, les fonctions germinales et somatiques sont assurées par deux noyaux distincts : un noyau germinal (MIC), qui transmet l’information génétique entre générations, et un noyau somatique (MAC), responsable de l’expression des gènes. À chaque cycle sexuel, le MAC est détruit et un nouveau MAC se forme à partir du MIC, avec une particularité notable : environ 30 % de l’ADN germinal est éliminé lors de la formation du nouveau noyau somatique.
Grâce à plus de dix ans d’efforts impliquant notamment des équipes du CEA, du CNRS et de l’INRAE, les scientifiques ont pu reconstituer des génomes germinaux complets pour plusieurs espèces du complexe d’espèces Paramecium aurelia, dont Paramecium tetraurelia. Ces assemblages révèlent un génome constitué d’environ 160 petits chromosomes, caractérisé par un taux de recombinaison exceptionnellement élevé.
Une voie inédite pour éliminer les extrémités chromosomiques
L’un des résultats majeurs de cette étude publiée dans la revue BMC Biology est la mise en évidence que les extrémités des chromosomes germinaux sont éliminées très tôt lors du développement du MAC. Ces régions contiennent un nouveau groupe d’éléments transposables, appartenant à la famille des Hélitrons. Bien que très anciens à l’échelle de l’évolution, ces éléments sont restés actifs dans le groupe d’espèces Paramecium aurelia et présentent une affinité particulière pour les régions télomériques.
Fait remarquable, leur élimination ne dépend pas de l’endonucléase PiggyMac, connue pour être essentielle à l’excision des autres éléments transposables chez ces organismes. Cette observation suggère l’existence d’une voie alternative d’élimination de l’ADN, encore inconnue, ouvrant de nouvelles perspectives de recherche sur les mécanismes moléculaires impliqués.
Enfin, ce phénomène ne semble pas limité aux ciliés. Des observations similaires ont été faites chez certains nématodes, où les extrémités chromosomiques sont également éliminées lors de la différenciation cellulaire. Cette convergence évolutive suggère que l’élimination ciblée des extrémités chromosomiques pourrait représenter une stratégie plus répandue qu’on ne le pensait pour remodeler les génomes au cours du développement.
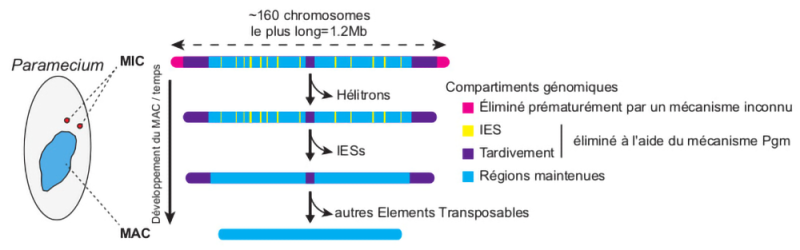
Figure : Les étapes d'élimination programmée d'ADN. Le compartiment aux extrémités identifié par l’étude est éliminé de manière très précoce, par un mécanisme qui reste à déterminer. L'élimination dépendante de l’endonucléase PiggyMac se déroule ensuite, ciblant d’abord des vestiges d’éléments transposables en copie unique (IES) puis les éléments transposables.
En savoir plus : Arnaiz, O., Guérin, F., Couloux, A. et al. The tiny germline chromosomes of Paramecium aurelia have an exceptionally high recombination rate and are capped by a new class of Helitrons. BMC Biol 24, 99 (2026). https://doi.org/10.1186/s12915-026-02584-w
Contact
Laboratoire
Institut Jacques Monod (CNRS/ Université Paris Cité)
15 rue Hélène Brion
75205 Paris Cedex 13
Institut de biologie intégrative de la cellule - I2BC (CEA/CNRS/Université Paris-Saclay)
1 Avenue de la Terrasse
91198 Gif-sur-Yvette

