Une marque épigénétique qui active pour mieux réprimer
Chez les eucaryotes, la marque épigénétique H3K27me3 est classiquement associée à la répression transcriptionnelle. Chez l’eucaryote unicellulaire Paramecium tetraurelia, les scientifiques montrent qu’un complexe protéique qui lie cette marque participe à une boucle de rétrocontrôle positif, couplant transcription et accumulation de la marque répressive au niveau des éléments transposables. Cette étude, publiée dans Genome Biology, révèle la diversité des stratégies épigénétiques contrôlant la stabilité du génome.
Une marque répressive aux fonctions bien établies…mais incomplètement comprises
La modification d’histone H3K27me3, déposée par le complexe Polycomb Repressive Complex 2 (PRC2), est classiquement associée à la répression transcriptionnelle. Si son implication dans la répression des gènes est bien documentée chez de nombreux eucaryotes, les mécanismes par lesquels H3K27me3 contribue à la répression des éléments transposables restent encore mal compris.
Un mécanisme original mis en évidence chez Paramecium
Chez l’eucaryote unicellulaire cilié Paramecium tetraurelia, où PRC2 cible les éléments transposables et les répriment, des scientifiques mettent en évidence un mécanisme original reliant cette marque épigénétique répressive à la transcription.
Ils identifient un complexe protéique organisé autour de la protéine à chromodomaine, Firefly, capable de se lier directement à H3K27me3. Ce complexe s’accumule au niveau des éléments transposables et, de manière inattendue, promeut leur transcription naissante et le recrutement du complexe PRC2, couplant ainsi transcription et accumulation de H3K27me3.
Un éclairage nouveau sur les stratégies évolutives mises en place pour protéger le génome
Chez de nombreux eucaryotes, la répression des éléments transposables repose plutôt sur des mécanismes impliquant une autre marque répressive, H3K9me3. L’implication de H3K27me3 dans la répression transcriptionnelle des éléments transposables démontre la diversité évolutive des stratégies de contrôle de ces éléments. De manière remarquable, des principes communs associant transcription transitoire et mise en place de marques répressives à travers des boucles de rétrocontrôle positifs sont conservés évolutivement.
Ces travaux, publiés dans Genome Biology, révèlent ainsi l’existence d’une boucle de rétrocontrôle positif dans laquelle la lecture de H3K27me3 stimule une transcription nécessaire au renforcement de cette même marque. Ils apportent un éclairage nouveau sur les fonctions de Polycomb et sur les stratégies évolutives mises en place pour protéger le génome contre les éléments mobiles et préserver son intégrité.
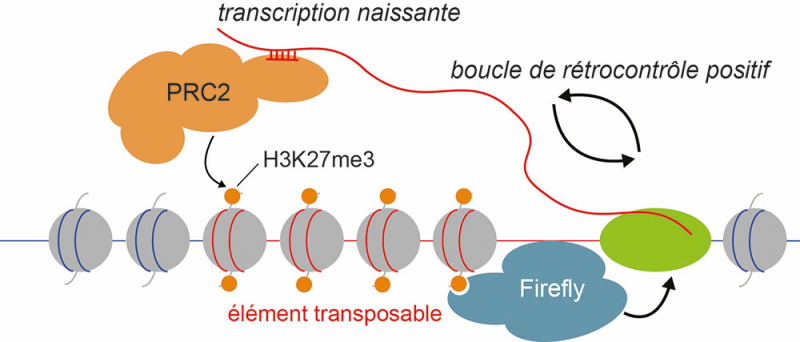
Figure : Modèle pour le mode d’action du complexe Firefly. Le complexe formé de la protéine à chromodomaine Firefly, la protéine à domaine coiled coil Sleepy et le facteur d’élongation de la transcription TfIIs4 est requis pour la transcription naissante des éléments transposables. Les transcrits naissants guident le recrutement du complexe PRC2 vers les éléments où les modifications répressives H3K27me3 sont déposées. La liaison du chromodomaine de Firefly à H3K27me3 engage le complexe Firefly dans une boucle de rétrocontrôle positif qui couple l’accumulation de H3K27me3 et la transcription naissante des éléments transposables.
En savoir plus : Balan, T., Petitalot, A., Albert, J.R. et al. A H3K27me3 reader complex couples H3K27me3 accumulation to nascent transcription of transposable elements in Paramecium. Genome Biol (2026). https://doi.org/10.1186/s13059-026-04045-7
Contact
Laboratoire
Institut Jacques Monod - IJM (CNRS/Université Paris Cité)
15 rue Hélène Brion,
75013 Paris